김빛내리 교수 주도, 기존 코로나바이러스 연구 오류까지 잡아내
미국 질병예방통제센터(CDC) 제공
IBS-질본, 코로나바이러스 유전자지도 완성
기초과학연구원(IBS)와 질병관리본부 공동연구팀이 코로나바이러스와 관련한 완벽한 유전자지도를 완성해 발표했다.
미국 질병예방통제센터(CDC) 제공
미국 질병예방통제센터(CDC) 제공
질병관리본부가 기초과학연구원(IBS) RNA연구단과 함께 코로나19의 원인 바이러스인 사스 코로나바이러스 2(SARS-CoV-2)를 자세히 볼 수 있는 고해상도 유전자지도를 완성하고 권위있는 생물학 분야 국제학술지 ‘셀’ 9일자에 발표했다.
코로나19 바이러스는 DNA가 아니라 RNA형태의 유전자를 갖고 있다. 바이러스는 숙주세포에 침투해 유전정보가 담긴 유전체RNA를 복제하고 이를 바탕으로 다양한 하위유전체RNA를 만들어 낸다.
IBS 제공
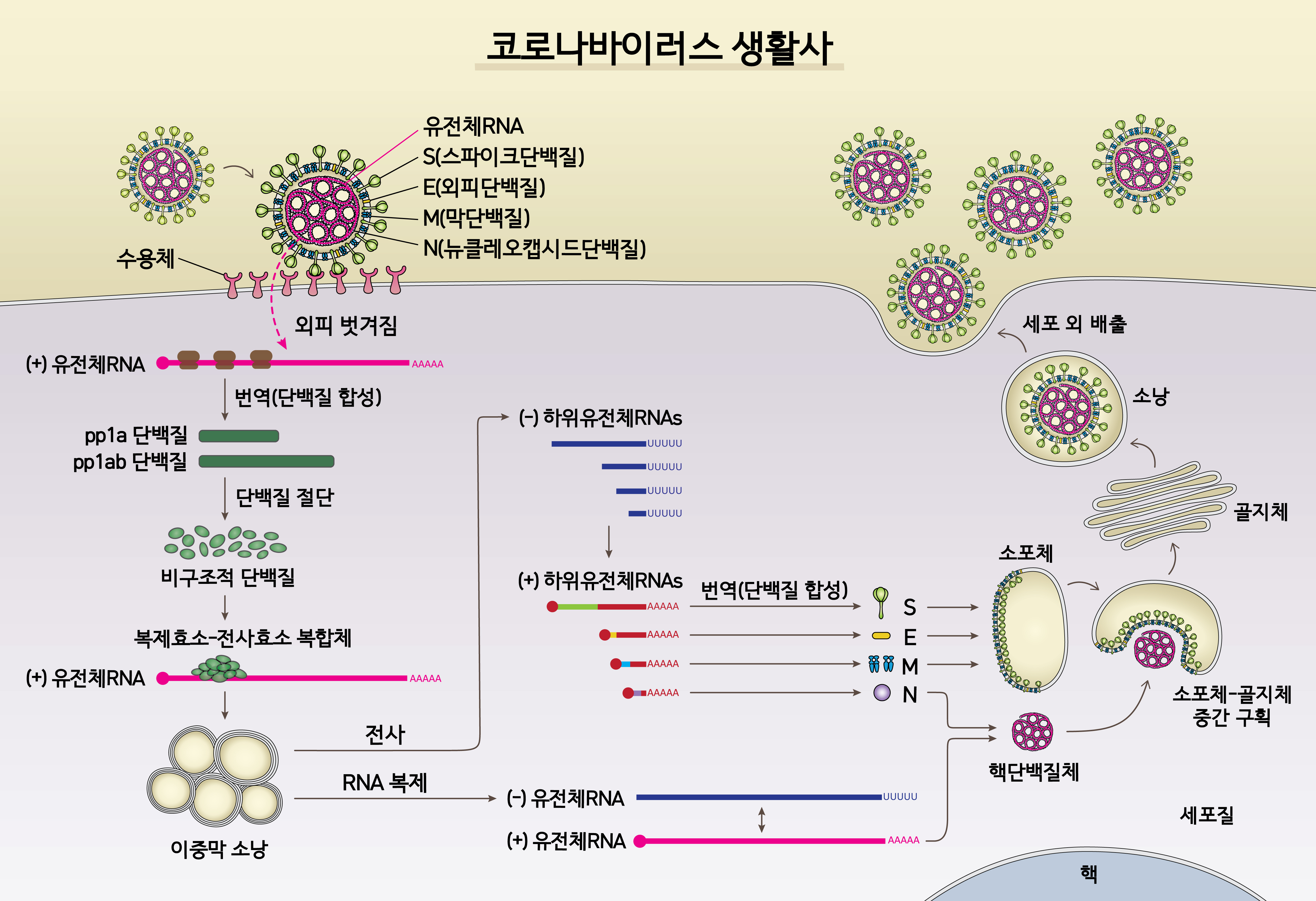
국내 연구진이 밝혀낸 코로나19 바이러스의 생활사
김빛내리 IBS 연구단장팀과 질병관리본부 공동연구팀이 코로나19 바이러스의 유전자 지도를 완성하고 바이러스의 생활사를 밝혀냈다.
IBS 제공
IBS 제공
기존에도 코로나19 바이러스의 유전체 정보에 대한 연구들은 있었지만 유전체 위치를 대략적으로 예측하는 수준에 머물렀다.
그러나 연구팀은 질병관리본부로부터 불활성화된 코로나19 바이러스를 분양받아 나노포어 직접RNA시퀀싱, 나노볼 DNA시퀀싱이라는 차세대 염기서열분석법을 활용해 숙주세포로 침투해 만들어진 RNA전사체 전체를 분석했다.
이를 통해 지금까지 알려지지 않은 수십 종의 RNA와 최소 41곳의 RNA 변형을 찾아내는 한편 유전체RNA상 유전자들이 어디에 위치하는지 정확히 찾아냈다. 기존에는 하위유전체RNA가 10개가 있다고 알려져 있었지만 이번 연구를 통해 하위유전체RNA는 9개만 있다는 것을 확인했다. 또 세포 내에서 융합과 삭제 등 다양한 형태의 유전자 재조합이 발생하고 RNA 수준에서 다양한 화학적 변화가 나타난다는 사실도 밝혀냈다.


연구를 이끈 김빛내리 IBS RNA 연구단장
유용하 기자 edmondy@seoul.co.kr




























![미국 맛 가미한 보물 찾기…한국 맛과 다른 백수 아빠[OTT 언박싱]](https://img.seoul.co.kr/img/upload//2024/02/16/SSC_20240216012138_N.jpg)









